記事一覧
R: インストールしたパッケージのバージョンを確認 「sessionInfo()」
現在、使用しているパッケージ(ライブラリ)のバージョンを確認したいことがあります。その時に使うコマンドが、 sessionInfo() です。
sessionInfo()確認したいパッケージを library(tidyverse) のように、読み込んだ状態で、 sessionInfo() を入力すると、ロードされているパッケージの名前と、バージョンが表示されます。(下記は、 tidyverse
ggplot2: オブジェクトの構造を表示する (str 関数)
R では、世界中のユーザーや研究者が提供したパッケージを、追加でインストールして、利用することができます。パッケージには複数の関数が含まれており、それらを使用して、データの解析ができます。
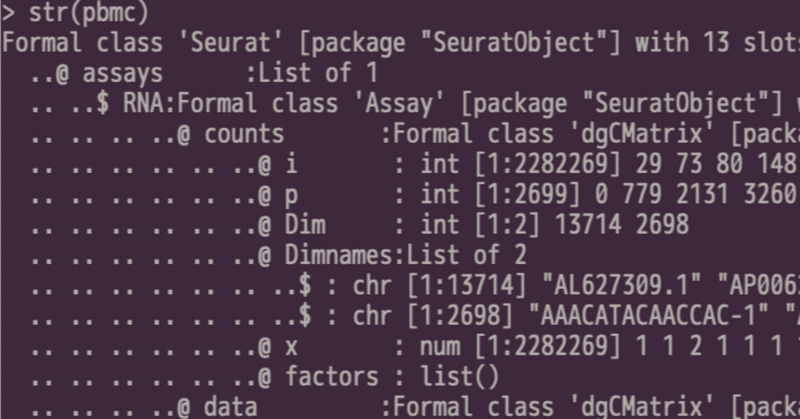
解析結果として出力されたオブジェクトが、どのようなデータを含んでいるか確認したい場合があります。その時、 str() 関数を用いると、オブジェクトの中身の構造を見ることができます。
str() 関数でオブジ
ggplot2: y = x の補助線を引く
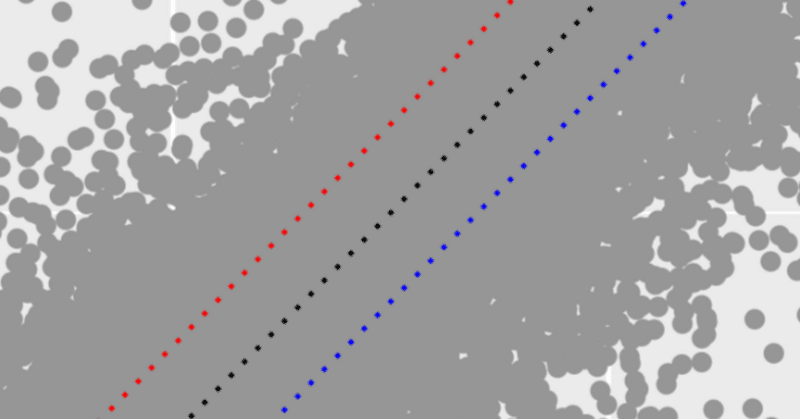
下記のような散布図があったとします。このうち、変動していない遺伝子は、normal (x軸)と tumor (y軸) の値が同じ、つまり、 y = x になっている点ということです。これを判断しやすいように、 y = x の補助線を引く例を紹介します。
geom_abline() で直線を追加y = x の直線を追加するには、 geom_point() にプラスで続けて、 geom_abline
ggplot2 を使って MA プロットを作成
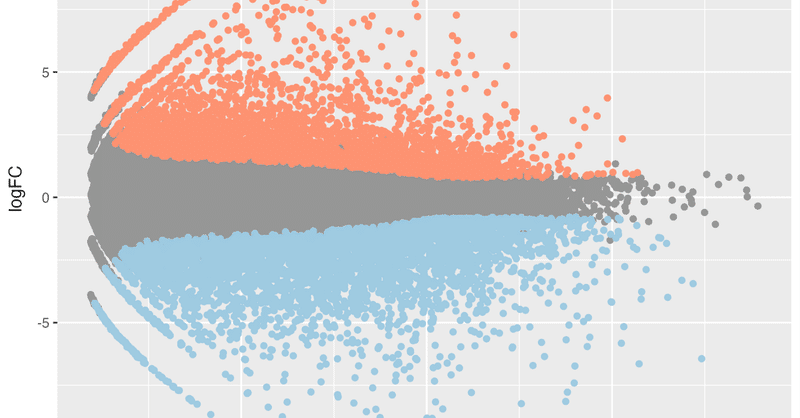
遺伝子発現の変動を表示する方法として、ボルケーノプロットを紹介しましたが、もう1つよく使われるプロットとして、MAプロットがあります。もともと、マイクロアレイのデータを表示するのに用いられていましたが、RNA-seq のデータにも用いられます。
MA プロットに用いるデータ遺伝子発現の変動をスコア化したデータは、logCPM, logFC, p-value などの値を含みます。このうち、MA プ
ボルケーノプロット:log変換の意味
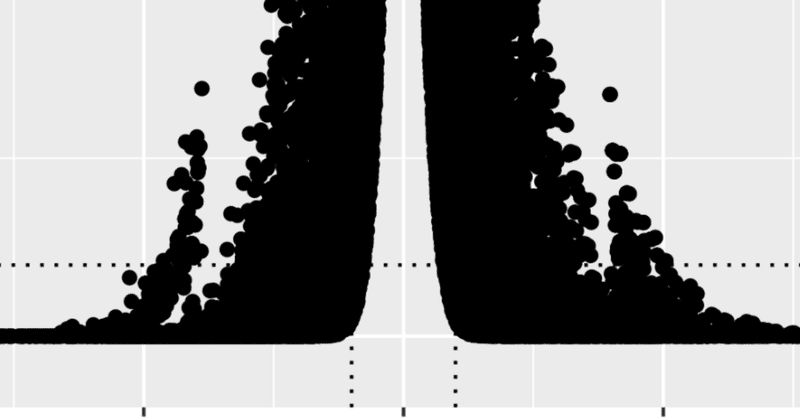
これまでに紹介したボルケーノプロットでは、 p-value をそのまま用いず、 log変換してプロットしています。その意味を解説します。
log変換しないとどうなるかまず、log変換しないとどうなるかを見てみましょう。-log10() の部分を削除すると、コードは下記のようになります。
g <- ggplot(de_result, aes(logFC, PValue))g + geom_poi
ggplot2: デフォルトのパレットの色
ggplot2 を使って、ボックスプロットや棒グラフ、パイチャートを作成した時、対象ごとに色をつけるように設定すると、自動的に選ばれた色が使用されます。
これらと同じ色を自分でも使いたかったり、16進数ではどのような値になるのか確認したい場合もあると思います。このパレットの値を取得する方法の紹介です。
hue_pal() 関数でパレットを生成デフォルトで使用されているパレットは、scales